Dinucleòtid de nicotinamida i adenina
| Substància química | grup d'entitats químiques i grup o classe d'entitats químiques |
|---|---|
| Estructura química | |
 | |
| NFPA 704: Standard System for the Identification of the Hazards of Materials for Emergency Response () | |
El dinucleòtid de nicotinamida i adenina[1] abreujada com NAD és un coenzim d'oxidoreducció present en totes les cèl·lules vives. És un dinucleòtid, ja que està compost de dos nucleòtids enllaçats pels seus grups fosfat. Un dels nucleòtids conté una adenina mentre que l'altre nucleòtid conté una nicotinamida.
En el metabolisme, el NAD+ intervé en les reaccions redox, en les quals transporta electrons d'una reacció a una altra. Així doncs, a les cèl·lules el coenzim és present en dues formes diferents (NAD+ i NADH). El NAD+ és un agent oxidant —accepta electrons d'altres molècules, quedant així reduït. Aquesta reacció forma el NADH, que pot ser utilitzat com a agent reductor per a cedir electrons. Aquesta transferència d'electrons és la funció principal del NAD+. Tot i així, el NAD+ també intervé en altres processos cel·lulars, com ara la seva funció com a substrat d'enzims que afegeixen o eliminen grups químics a les proteïnes durant les modificacions postraduccionals. A causa de la importància d'aquestes funcions, els enzims que intervenen en el metabolisme del NAD+ són un objectiu molt important en la investigació de nous fàrmacs.
Als organismes vius, el NAD+ es pot sintetitzar ex novo a partir dels aminoàcids triptòfan o àcid aspàrtic. De manera alternativa, components més complexos del coenzim es poden obtenir dels aliments (per exemple, la vitamina niacina). Altres components similars són alliberats en reaccions en les quals té lloc un trencament de l'estructura del NAD+. Aquests components més complexos passen a una via de recuperació que els recicla en la forma activa del coenzim. Algunes molècules de NAD+ es converteixen a fosfat de dinucleòtid de nicotinamida i adenina (NADP+); l'estructura química d'aquest coenzim relacionat amb el NAD+ és similar a la del NAD+, però té un paper diferent al metabolisme.
Estructura[modifica]
La figura de la dreta presenta l'estructura del NAD+ (forma oxidada). Aquest coenzim no es fixa sobre l'apoenzim, és un cosubstrat.
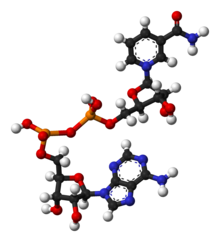

El dinucleòtid de nicotinamida i adenina, com la resta de dinucleòtids, està format per dos nucleòtids units pels seus grups fosfats. Els dos nucleòtids estan formats per ribosa; en un nucleòtid, la ribosa té adenina unida al primer àtom de carboni (en posició 1) i en l'altre nucleòtid la ribosa té nicotinamida unida en la mateixa posició. El grup nicotinamida pot estar unit amb dues possibles orientacions a aquest àtom de carboni anomèric. A causa de l'existència d'aquestes dues possibles estructures diferents, el compost NAD+ presenta dos diastereòmers. Als organismes només és present el diastereòmer β-nicotinamida. Els dos nucleòtids que componen el NAD+ estan units pels seus carbonis 5' mitjançant un enllaç de dos grups fosfats.[2]
Acció redox[modifica]

En el metabolisme, el NAD accepta o cedeix electrons a les reaccions redox.[3] Aquestes reaccions (resumides a la fórmula inferior) impliquen l'extracció del reactiu de dos àtoms d'hidrogen, en forma d'un ió hidrur (H-) i d'un protó (H+). El protó és alliberat a la solució en la qual té lloc la reacció, mentre que el reductor RH2 és oxidat i el NAD+ és reduït a NADH mitjançant la transferència dels hidrurs a l'anell de nicotinamida.
- RH2 + NAD+ → NADH + H+ + R
Del parell d'electrons de l'hidrur, un electró és transferit al nitrogen carregat positivament de l'anella de nicotinamida del NAD+ i el segon àtom d'hidrogen és transferit al carboni C4, l'àtom oposat al nitrogen. El potencial mitjà del parell redox NAD+/NADH és –0.32 volts, cosa que mostra que el NADH és un fort agent reductor.[4] Aquesta reacció redox és fàcilment reversible, el NADH pot reduir una molècula i ser reoxidat, obtenint així NAD+. Això implica que el coenzim pot mantenir-se en un cicle entre les formes NAD+ i NADH sense ser consumit.
Propietats físiques[modifica]
D'aspecte, totes les formes d'aquest coenzim són una pols blanca amorfa, higroscòpica i molt soluble en aigua.[5] En estat sòlid, són químicament estables si es mantenen en un lloc sec i sense llum. Les dissolucions de NAD+ són incolores i estables durant aproximadament una setmana a 4 °C i pH neutre, però es descomponen ràpidament si estan en contacte amb àcids o bases. Quan es descomponen, els productes obtinguts són inhibidors enzimàtics.[6]
Interès en bioquímica analítica[modifica]
Com a propietat física particular, el NAD+ posseeix un màxim d'absorció en l'espectre de la radiació ultraviolada a 259 nm (amb un coeficient d'extinció de 16900 M-1cm-1);[7] la forma reduïda (NADH) té dos màxims d'absorció ultraviolat, un primer màxim a 259 nm i un segon a 339 nm (amb un coeficient d'extinció de 6,220 M-1cm-1).[7] Tant el NAD+ com el NADH absorbeixen la radiació electromagnètica en l'espectre de la llum ultraviolada a causa de la presència de la base adenina.

Aquesta diferència en l'absorció de la llum ultraviolada de longituds d'ona elevades existent entre la forma oxidada i la reduïda del coenzim permet la mesura (de manera simple) de la conversió de forma oxidada a reduïda en experiments amb enzims (es pot mesurar mitjançant la quantitat d'absorció UV a 340 nm utilitzant un espectrofotòmetre).[7] Un augment d'absorbància indica una formació de NADH (la reacció va en el sentit de la reducció del substrat) mentre que una disminució de l'absorbància indica consum de NADH amb formació de NAD+ (la reacció va en el sentit de l'oxidació del substrat). La corba correspon a la cinètica d'aparició o desaparició del NADH. A partir d'aquesta corba, és possible calcular la velocitat inicial de la reacció (vegeu Cinètica de Michaelis-Menten).
El NAD+ i el NADH també difereixen en la seva fluorescència. El NADH en solució té un pic d'emissió a 460 nm i una vida de fluorescència de 0.4 ns, mentre que la forma oxidada del coenzim no presenta fluorescència.[8] Les propietats de fluorescència del NADH canvien quan aquest s'uneix a proteïnes, de manera que els canvis que es produeixen es poden utilitzar per a mesurar constants de dissociació, que són molt útils en l'estudi de la cinètica enzimàtica.[8][9] Aquests canvis en les propietats de fluorescència també s'utilitzen per a mesurar, mitjançant microscòpia de fluorescència, canvis en l'estat redox de les cèl·lules vives.[10]
Concentració i estat a les cèl·lules[modifica]
Al fetge de rata, la quantitat total de NAD+ i NADH és aproximadament 1 μmol per gram de pes (humit), aproximadament 10 vegades la concentració de NADP+ i NADPH en les mateixes cèl·lules.[11] La concentració exacta de NAD+ al citosol de les cèl·lules és molt difícil de mesurar; les estimacions més recents situen aquesta concentració als 0.3mM[12] [13] en cèl·lules animals i entre 1mM i 2 mM en llevats[3] Tot i així, cal tenir en compte que més del 80 per cent del coenzim s'uneix a proteïnes, de manera que la concentració en dissolució és, en realitat, considerablement més baixa.[14] Les dades referents a la concentració d'aquest coenzim en altres compartiments cel·lulars són molt limitades, tot i que se sap que al mitocondri la concentració de NAD+ és similar a la del citosol.[13] Aquest NAD+ mitocondrial és transportat al mitocondri per una proteïna de membrana transportadora específica, ja que el coenzim no pot travessar la membrana per difusió.[15] El balanç entre la forma oxidada i la forma reduïda del dinucleòtid de nicotinamida i adenina s'anomena proporció NAD+/NADH. Aquesta proporció és una important component en el que s'anomena «estat redox» de la cèl·lula, una mesura que reflecteix tant l'activitat metabòlica de la cèl·lula com la salut cel·lular.[16] Els efectes de la proporció NAD+/NADH són complexos, ja que aquesta proporció controla l'activitat de diversos enzims clau, incloent el gliceraldehid-3-fosfat deshidrogenasa i el piruvat deshidrogenasa. En teixits de mamífers sans, la proporció NAD+/NADH estimada és generalment de 700; així doncs, aquesta proporció és favorable a les reaccions d'oxidació.[17][18] En canvi, la proporció NADP+/NADPH és aproximadament 0.005, de manera que el NADPH és la forma dominant d'aquest coenzim.[19] Aquestes diferents proporcions són fonamentals en els diferents papers metabòlics del NADH i el NADPH.
Biosíntesi[modifica]
El NAD+ és sintetitzat per dues vies metabòliques. Es pot produir o bé en una via de novo a partir d'aminoàcids o bé en una via de recuperació partir del reciclatge de components més complexos com la nicotinamida.
Síntesi de novo[modifica]

Molts organismes sintetitzen NAD+ a partir dels seus components bàsics.[3] El conjunt específic de reaccions químiques varia segons l'organisme, però una característica comuna és la síntesi d'àcid quinolínic (QA) a partir d'un aminoàcid —triptòfan (Trp) en animals i alguns bacteris o àcid aspàrtic en plantes i alguns bacteris.[20][21] L'àcid quinolínic és convertit en àcid nicotínic mononucleòtid (NaMN) mitjançant la transferència d'un grup fosforibosa. Seguidament, un grup adenilat és transferit per a formar àcid nicotínic adenina dinucleòtid (NaAD). Finalment, l'àcid nicotínic del NaAD és amidat, obtenint així un grup nicotinamida (Nam) i, per tant, dinucleòtid de nicotinamida i adenina .[3] Seguidament, a partir de part del NAD+ es sintetitza NADP+ gràcies a l'acció del NAD+cinasa, que fosforila el NAD+.[22] En la majoria d'organismes, aquest enzim utilitza ATP per a obtenir el grup fosfat, però en bacteris com ara Mycobacterium tuberculosis i en alguns arqueus com ara Pyrococcus horikoshii, també s'obté de polifosfat inorgànic.[23][24]
Vies de recuperació[modifica]

A part de la síntesi de novo de NAD+ a partir de precursors simples d'aminoàcids, les cèl·lules també recuperen components més complexeos que contenen nicotinamida. Tot i que es coneixen altres precursors, els tres components naturals que contenen anells de nicotinamida i que són utilitzats en les vies de recuperació són l'àcid nicotínic (Na), la nicotinamida (Nam) i la nicotinamida ribosida (NR).[25] Aquests precursors s'integren a la via de biosíntesi del NADP+ mitjançant reaccions d'adenilació i de fosforilació. Aquests components es poden obtenir de la dieta, en la qual la mescla d'àcid nicotínic i nicotinamida s'anomena vitamina B3 o niacina. Aquests components, però, també són sintetitzats a les cèl·lules, quan el grup nicotinamida és alliberat del NAD+ en reaccions de transferència de l'ADP-ribosa. Sembla que els enzims involucrats en aquestes vies de recuperació estan concentrats al nucli cel·lular, cosa que podria compensar la gran quantitat de reaccions que consumeixen NAD+ en aquest orgànul.[26] Les cèl·lules també poden obtenir NAD+ extracel·lular de les seves cèl·lules veïnes.[27] Tot i la presència de la via de síntesi de novo, les vies de recuperació són essencials en els humans; una manca de niacina a la dieta causa pel·lagra,[28] una malaltia basada en una deficiència vitamínica. El gran requeriment de NAD+ és el resultat del constant consum del coenzim en reaccions com les modificacions postraduccionals, ja que el cicle de nicotinamida adenina dinucleòtid entre la seva forma oxidada i la seva forma reduïda a les reaccions redox no canvia els nivells totals de coenzim.[3] Les vies de recuperació dels microorganismes són diferents de les dels mamífers.[29] Alguns patògens, com el llevat Candida glabrata o el bacteri Haemophilus influenzae són auxòtrofs del NAD+ - no en poden sintetitzar – però tenen vies de recuperació i, per tant, depenen de fonts externes de NAD+ o dels seus precursors.[30][31] Encara més sorprenent és el cas del patogen intracel·lular Chlamydia trachomatis, que no sembla tenir cap gen involucrat en les vies de síntesi o de recuperació ni del NAD+ ni del NADP+ i aparentment necessita obtenir tots dos coenzims del seu hoste.[32]
Funcions[modifica]
El dinucleòtid de nicotinamida i adenina té diversos papers essencials en el metabolisme. Actua com a coenzim a les reaccions redox, com a donador de grups d'ADP-ribosa a les reaccions d'ADP-ribosilació, com a precursor de la molècula missatgera secundària ADP-ribosa cíclica i també pot actuar com a substrat per a les ADN lligases bacterianes i per a un grup d'enzims anomenats sirtuines, que utilitzen el NAD+ per a extreure grups acetil de les proteïnes.
Oxidoreductases[modifica]
Per a més informació: oxidoreductasa

El paper principal del NAD+ al metabolisme és la transferència d'electrons d'una molècula a una altra. Les reaccions d'aquest tipus són catalitzades per un grup d'enzims anomenat oxidoreductases. El nom correcte d'aquests enzims conté els noms dels seus dos substrats: per exemple, el NADH:ubiquinona oxidoreductasa catalitza l'oxidació del NADH pel coenzim Q.[34] Tot i així, aquests enzims també s'anomenen deshidrogenases o reductases, de manera que el NADH:ubiquinona oxidoreductasa sovint s'anomena NADH deshidrogenasa o, en alguns casos, coenzim Q reductasa.[35]
Quan estan units a una proteïna, el NAD+ i el NADH estan continguts en una estructura coneguda com a plegament de Rossmann.[36] Aquest tipus de plegament s'anomena així en honor de Michael Rossmann, que va ser el primer científic a veure que es tractava d'una estructura molt comuna en les proteïnes unides a nucleòtids.[37] El plegament de Rossmann està format per tres o més cadenes beta paral·leles enllaçades per dues hèlix alfa seguint l'ordre beta - alfa – beta –alfa - beta. Aquesta estructura forma un full beta flanquejat per una capa d'hèlixs alfa a cada costat. Com que cada plegament de Rossmann s'uneix a un nucleòtid, els dominis d'unió per al dinucleòtid NAD+ consisteixen en un parell de plegaments de Rossmann, cadascun dels quals uneix el nucleòtid amb el cofactor.[37] Aquest tipus de plegament no és universal entre els enzims dependents de NAD; recentment s'ha descobert un tipus d'enzims de bacteris implicats en el metabolisme dels aminoàcids que s'uneixen al coenzim, però que no tenen aquest plegament.[38]
Quan s'uneix a un centre actiu d'una oxidoreductasa, l'anell de nicotinamida del coenzim és posicionat de manera que pugui acceptar un hidrur provinent de l'altre substrat. El carboni C4 que accepta l'hidrogen és proquiral; aquest fet es pot utilitzar en el camp de la cinètica enzimàtica per a obtenir informació sobre el mecanisme de l'enzim. Això es fa barrejant un enzim amb un substrat que tingui deuteris en lloc d'àtoms d'hidrogen, de manera que l'enzim redueixi el NAD+ transferint els deuteris en lloc dels hidrògens. En aquest cas, un enzim és capaç de produir un dels dos estereoisòmers del NADH. En alguns enzims, l'hidrogen és transferit des de la part superior del pla de l'anell de nicotinamida; aquest tipus d'enzims s'anomenen oxidoreductases de classe A, mentre que els enzims de classe B transfereixen l'àtom d'hidrogen des de la part inferior del pla.[39]

Malgrat les semblances en la manera d'unir els dos coenzims a les proteïnes, els enzims gairebé sempre presenten un elevat nivell d'especificitat pel NAD+ o el NADP+.[40] Aquesta especificitat mostra els diferents papers metabòlics dels dos coenzims, i és el resultat dels diferents conjunts de residus d'aminoàcids que hi ha els dos tipus d'unió amb el coenzim. Per exemple, al centre actiu dels enzims dependents de NADP+, es forma un enllaç iònic entre una cadena lateral d'un aminoàcid bàsic i el grup fosfat àcid del NADP+. En canvi, en els enzims dependents de NAD+, la càrrega al centre actiu és la contrària, impedint així que el NADP+ s'hi uneixi. Malgrat tot, hi ha algunes excepcions a aquesta regla general i, en algunes espècies, els enzims com l'aldosa reductasa, la glucosa-6-fosfat deshidrogenasa i la metiltetrahidrofolat reductasa poden utilitzar els dos coenzims.[41]
Paper en el metabolisme redox[modifica]
Per a més informació: respiració cel·lular i fosforilació oxidativa

Les reaccions redox catalitzades per oxidoreductases són vitals en totes les àrees del metabolisme, però especialment quan té lloc una alliberació d'energia a partir de nutrients. En aquestes reaccions, compostos reduïts com ara la glucosa són oxidats, alliberant així energia. Aquesta energia és transferida al NAD+ per la reducció del NADH, cosa que forma part de la glucòlisi i del cicle de Krebs. Als eucariotes, els electrons transportats pel NADH que és sintetitzat al citoplasma per la glicòlisi són transferits a l'interior del mitocondri (per a reduir el NAD+ mitocondrial) mitjançant llançadores mitocondrials, com per exemple la llançadora malat – aspartat.[42] El NADH mitocondrial és seguidament oxidat per una cadena transportadora d'electrons, que bomba protons a través de la membrana i genera ATP per fosforilació oxidativa.[43] Aquests sistemes de llançadora també tenen la mateixa funció de transport als cloroplasts.[44] Com que en aquests conjunts de reaccions relacionades als quals s'ha fet referència s'utilitzen tant la forma oxidada com la reduïda del dinucleòtid de nicotinamida i adenina, la cèl·lula manté aproximadament iguals les concentracions de NAD+ i NADH; l'elevada proporció NAD+/NADH permet al coenzim d'actuar tant com a agent reductor com oxidant.[45] En canvi, la principal funció del NADPH és com a agent reductor en l'anabolisme, estant aquest coenzim involucrat en vies metabòliques com la síntesi dels àcids grassos o la fotosíntesi. Com que el NADPH és necessari com a potent agent reductor per a dur a terme reaccions redox, la proporció NADP+/NADPH es manté força baixa.[45] Tot i que és important al catabolisme, el NADH també s'utilitza en reaccions anabòliques, com ara la gluconeogènesi.[46] Aquesta necessitat de NADH en l'anabolisme suposa un problema per als procariotes que creixen en medis nutritius que alliberen només petites quantitats d'energia. Per exemple, els bacteris nitrificants com ara Nitrobacter oxiden nitrit a nitrat, procés en el qual s'allibera prou energia per a bombar protons i generar ATP, però no suficient energia per a sintetitzar NADH de manera directa.[47] Com que el NADH és necessari per a les reaccions anabòliques, aquests bacteris utilitzen una nitrit oxidoreductasa per a produir prou força protomotriu per a fer funcionar part de la cadena transportadora d'electrons en sentit invers, generant així NADH.[48]
Paper en el metabolisme no redox[modifica]
El coenzim NAD+ també és consumit en reaccions de transferència de l'ADP-ribosa. Per exemple, els enzims anomenats ADP-ribosil transferases afegeixen el grup ADP-ribosa del coenzim a les proteïnes, en una modificació postraduccional anomenada ADP-ribosilació.[49] El NAD+ també pot ser afegit a l'ARN cel·lular en un procés de modificació de base.[50] L'ADP-ribosilació implica o bé l'addició d'una sol grup ADP-ribosa, a la mono-ADP-ribosilació, o la transferència de l'ADP-ribosa a proteïnes en cadenes llargues, que s'anomena poli-ADP-ribosilació.[51] La mono-ADP-ribosliació es va identificar per primera vegada en el mecanisme d'un conjunt de toxines bacterianes, entre les quals cal destacar la toxina del còlera, però també està implicada en la senyalització cel·lular de cèl·lules normals.[52][53] La poli-ADP-ribosilació té lloc gràcies a l'acció de les poli(ADP-ribosa) polimerases.[54][51] L'estructura poli(ADP-ribosa) està implicada en la regulació de diversos processos cel·lulars i és molt important al nucli cel·lular, en processos com la reparació del ADNi el manteniment dels telòmers.[54] A més d'aquestes funcions a l'interior de la cèl·lula, s'ha descobert recentment un grup d'ADP-ribosil transferases extracel·lulars, però les seves funcions són encara desconegudes.[55]
Una altra funció d'aquest coenzim en la senyalització cel·lular és com a precursor de l'ADP-ribosa cíclica, que es sintetitza a partir del NAD+ per l'acció d'ADP-ribosil ciclases, com a part d'un sistema de segons missatgers.[56] Aquesta molècula actua en la senyalització de calci, alliberant calci de dipòsits intracel·lulars.[57] Això es fa mitjançant la unió i l'obertura d'un tipus de canal de calci anomenats receptors de rianodina, presents a les membranes dels orgànuls com el reticle endoplasmàtic.[58] El NAD+ també és consumit per les sirtuines, que són desacetilases dependents de NAD+, com per exemple la Sir2.[59] Aquests enzims actuen transferint un grup acetil des de la seva proteïna substrat al grup ADP-ribosa del NAD+; això trenca el coenzim i causa l'alliberació de nicotinamida i O-acetil-ADP ribosa. Les sirtuines semblen intervenir principalment en la regulació de la transcripció mitjançant la desacetilació de les histones i l'alteració de l'estructura del nucleosoma.[60] Tot i així, proteïnes que no són histones també poden ser desacetilades per les sirtuines. Aquestes activitats de les sirtuines són d'interès particularment per la seva importància en la regulació de l'envelliment.[61] Les ADN ligases bacterianes, entre d'altres, són enzims dependents del NAD que uneixen dos extrems d'ADN utilitzant el NAD com a substrat per a donar una adenosina monofosfat (AMP) al fosfat 5′ d'un extrem del DNA. Aquest intermediari és seguidament atacat pel grup hidroxil 3′ de l'altre extrem de DNA, formant un nou enllaç fosfodièster.[62] Aquest mecanisme contrasta amb les ADN ligases eucariotes, que utilitzen ATP per a formar l'ADN-AMP intermediari.[63]
Farmacologia[modifica]
Els enzims que sintetitzen i utilitzen NAD+ i NADH són importants tant en la farmacologia actual com en la recerca de futurs tractaments per a malalties.[64] Hi ha tres aspectes destacats en el desenvolupament de nous fàrmacs, en el disseny d'inhibidors o activadors enzimàtics basats en la seva estructura que modifiquin l'activitat dels enzims dependents de NAD+ i intentant inhibir la biosíntesi del NAD+.[65] Actualment, el coenzim NAD+ en si no s'utilitza com a tractament per a cap malaltia. Tot i així, és un coenzim potencialment útil en la teràpia de malalties neurodegeneratives, com l'Alzheimer o el Parkinson[3] Les evidències científiques referents a la utilitat del NAD+ per a tractar processos degeneratius són molt ambivalents: els estudis en ratolins són prometedors,[66] mentre que un estudi clínic controlat versus placebo va fracassar, sense mostrar cap efecte del coenzim.[67] El NAD+ també és un element clau en el fàrmac isoniazida, que és utilitzat en el tractament de la tuberculosi, una infecció causada pel Mycobacterium tuberculosis. La isoniazida és un profàrmac que, un cop ha entrat al bacteri, és activat per una peroxidasa, que l'oxida a una forma de radical lliure.[68] Aquest radical reacciona amb el NADH per a produir adductes que són inhibidors molt potents dels enzims enoil-ACP reductasa[69] i dihidrofolat reductasa.[70] Com que un gran nombre d'oxidoreductases utilitzen NAD+i NADH com a substrats i s'hi uneixen mitjançant una estructura altament conservativa, el fet que els inhibidors basats en el NAD+ podrien ser específics per a un enzim és sorprenent.[71] Malgrat tot, això és possible: per exemple, els inhibidors basats en els compostos àcid micofenòlic i tiazofurina inhibeixen l'IMP deshidrogenasa al domini d'unió am el NAD+. A causa de la importància d'aquest enzim en el metabolisme de purines, aquests compostos poden ser molt útils en fàrmacs anticancerosos, antivirals i immunosupressors.[71][72] Altres fàrmacs no són inhibidors enzimàtics, però en lloc d'això activen enzims implicats en el metabolisme del NAD+. Les sirtuines són un objectiu particularment interessant en el desenvolupament d'aquests fàrmacs, ja que l'activació d'aquestes deacetilases dependents de NAD+ allarga la seva supervivència.[73] Compostos com ara el resveratrol augmenten l'activitat d'aquests enzims, cosa que pot ser important tenint en compte la seva capacitat de retardar l'envelliment tant en organismes model vertebrats,[74] com invertebrats.[75][76] A causa de les diferències en les vies metabòliques de la biosíntesi del NAD+ entre organismes (per exemple, entre bacteris i humans) aquesta àrea del metabolisme és un sector prometedor en el desenvolupament d'antibiòtics nous.[77][78] Per exemple, l'enzim nicotinamidasa, que converteix nicotinamida en àcid nicotínic, és un objectiu en el disseny de fàrmacs, ja que es tracta d'un enzim absent en humans però present en llevats i bacteris.[29]
Història[modifica]

El coenzim NAD+ va ser descobert pels bioquímics britànics Arthur Harden i William Youndin el 1906.[79] Aquests bioquímics van observar que afegir un extracte de llevat bullit i filtrat accelerava considerablement la fermentació alcohòlica en extractes de llevats no bullits. Van anomenar coferment al factor no identificat responsable d'aquest efecte. Mitjançant una llarga i dificultosa purificació d'extractes de llevats, Hans von Euler-Chelpin va identificar aquest factor estable a la calor com un nucleòtid sucre fosfat.[80] El 1936, el científic alemany Otto Heinrich Warburg va mostrar la funció del coenzim en la transferència d'hidrurs i va identificar la nicotinamida com a l'emplaçament de les reaccions redox.[81] El 1938 es va identificar una font de nicotinamida, quan Conrad Elvehjem va purificar niacina a partir del fetge i va demostrar que aquesta vitamina conté àcid nicotínic i nicotinamida.[82] El 1939, va aportar el primer argument de pes que sostenia que la niacina s'utilitzava per a sintetitzar el NAD+.[83] A principis de la dècada de 1940, Arthur Kornberg va fer una altra contribució notable en la comprensió del metabolisme del NAD+, essent el primer a detectar un enzim en una via de biosíntesi.[84] Posteriorment, el 1949, els bioquímics americans Morris Friedkin i Albert L. Lehninger van demostrar que el NADH unia vies metabòliques, per exemple, el cicle de Krebs amb la síntesi d'ATP per fosforilació oxidativa.[85] Finalment, el 1959, Jack Preiss i Philip Handler van descobrir els intermediaris i els enzims que intervenen en la biosíntesi del NAD+;[86][87] per això la síntesi de novo del NAD+ sovint s'anomena via de Preiss-Handler, en el seu honor. Els diferents papers del NAD(P) no relacionats amb redox s'han descobert recentment.[2] La primera d'aquestes funcions que va ser identificada (en la dècada de 1960) va ser la funció del NAD+ com a l'ADP-ribosa donador a les reaccions de l'ADP-ribosilació.[88] Estudis posteriors fets durant les dècades de 1980 i 1990 van revelar les activitats dels metabòlits del NAD+ i del NADP+ en la senyalització cel·lular —com ara l'acció de l'ADP-ribosa cíclica, que es va descobrir al 1987.[89] El metabolisme del NAD+ és encara al segle xxi una àrea important de recerca. L'interès dels científics pel NAD+ ha augmentat considerablement amb la descoberta (feta per Shinichiro Imai i col·laboradors al Massachusetts Institute of Techonolgy el 2000) de les proteïnes diacilcetases dependents de NAD anomenades sirtuines.[90]
Vegeu també[modifica]
Notes i referències[modifica]
- ↑ «Cercaterm | NAD». TERMCAT. [Consulta: 7 octubre 2022].
- ↑ 2,0 2,1 Pollak, N; Dölle C, Ziegler M «The power to reduce: pyridine nucleotides—small molecules with a multitude of functions». Biochem. J., 402, 2, 2007, pàg. 205–18. DOI: 10.1042/BJ20061638. PMC: 1798440. PMID: 17295611.
- ↑ 3,0 3,1 3,2 3,3 3,4 3,5 Belenky P; Bogan KL, Brenner C «NAD+ metabolism in health and disease» (PDF). Trends Biochem. Sci., 32, 1, 2007, pàg. 12–9. DOI: 10.1016/j.tibs.2006.11.006. PMID: 17161604 [Consulta: 23 desembre 2007].
- ↑ Unden G; Bongaerts J «Alternative respiratory pathways of Escherichia coli: energetics and transcriptional regulation in response to electron acceptors». Biochim. Biophys. Acta, 1320, 3, 1997, pàg. 217–34. DOI: 10.1016/S0005-2728(97)00034-0. PMID: 9230919.
- ↑ Windholz, Martha. The Merck Index: an encyclopedia of chemicals, drugs, and biologicals. 10th. Rahway NJ, US: Merck, 1983, p. 909. ISBN 911910271.
- ↑ Biellmann JF, Lapinte C, Haid E, Weimann G «Structure of lactate dehydrogenase inhibitor generated from coenzyme». Biochemistry, 18, 7, 1979, pàg. 1212–7. DOI: 10.1021/bi00574a015. PMID: 218616.
- ↑ 7,0 7,1 7,2 Dawson, R. Ben. Data for biochemical research. 3rd. Oxford: Clarendon Press, 1985, p. 122. ISBN 0-19-855358-7.
- ↑ 8,0 8,1 Lakowicz JR, Szmacinski H, Nowaczyk K, Johnson ML «Fluorescence lifetime imaging of free and protein-bound NADH». Proc. Natl. Acad. Sci. U.S.A., 89, 4, 1992, pàg. 1271–5. DOI: 10.1073/pnas.89.4.1271. PMC: 48431. PMID: 1741380.
- ↑ Jameson DM, Thomas V, Zhou DM «Time-resolved fluorescence studies on NADH bound to mitochondrial malate dehydrogenase». Biochim. Biophys. Acta, 994, 2, 1989, pàg. 187–90. PMID: 2910350.
- ↑ Kasimova MR, Grigiene J, Krab K, et al. «The free NADH concentration is kept constant in plant mitochondria under different metabolic conditions». Plant Cell, 18, 3, 2006, pàg. 688–98. DOI: 10.1105/tpc.105.039354. PMC: 1383643. PMID: 16461578.
- ↑ Reiss PD, Zuurendonk PF, Veech RL «Measurement of tissue purine, pyrimidine, and other nucleotides by radial compression high-performance liquid chromatography». Anal. Biochem., 140, 1, 1984, pàg. 162–71. DOI: 10.1016/0003-2697(84)90148-9. PMID: 6486402.
- ↑ Yamada K, Hara N, Shibata T, Osago H, Tsuchiya M «The simultaneous measurement of nicotinamide adenine dinucleotide and related compounds by liquid chromatography/electrospray ionization tandem mass spectrometry». Anal. Biochem., 352, 2, 2006, pàg. 282–5. DOI: 10.1016/j.ab.2006.02.017. PMID: 16574057.
- ↑ 13,0 13,1 Yang H, Yang T, Baur JA, Perez E, Matsui T, Carmona JJ, Lamming DW, Souza-Pinto NC, Bohr VA, Rosenzweig A, de Cabo R, Sauve AA, Sinclair DA. «Nutrient-Sensitive Mitochondrial NAD+ Levels Dictate Cell Survival». Cell, 130, 2007, pàg. 1095–107. DOI: 10.1016/j.cell.2007.07.035.
- ↑ Blinova K, Carroll S, Bose S, et al. «Distribution of mitochondrial NADH fluorescence lifetimes: steady-state kinetics of matrix NADH interactions». Biochemistry, 44, 7, 2005, pàg. 2585–94. DOI: 10.1021/bi0485124. PMID: 15709771.
- ↑ Todisco S, Agrimi G, Castegna A, Palmieri F «Identification of the mitochondrial NAD+ transporter in Saccharomyces cerevisiae». J. Biol. Chem., 281, 3, 2006, pàg. 1524–31. Arxivat de l'original el 2020-04-13. DOI: 10.1074/jbc.M510425200. PMID: 16291748 [Consulta: 15 desembre 2009]. Arxivat 2020-04-13 a Wayback Machine.
- ↑ Schafer F, Buettner G «Redox environment of the cell as viewed through the redox state of the glutathione disulfide/glutathione couple». Free Radic Biol Med, 30, 11, 2001, pàg. 1191–212. DOI: 10.1016/S0891-5849(01)00480-4. PMID: 11368918.
- ↑ Williamson DH, Lund P, Krebs HA «The redox state of free nicotinamide-adenine dinucleotide in the cytoplasm and mitochondria of rat liver». Biochem. J., 103, 2, 1967, pàg. 514–27. PMID: 4291787.
- ↑ Zhang Q, Piston DW, Goodman RH «Regulation of correpressor function by nuclear NADH». Science, 295, 5561, 2002, pàg. 1895–7. PMID: 11847309.
- ↑ Veech RL, Eggleston LV, Krebs HA «The redox state of free nicotinamide-adenine dinucleotide phosphate in the cytoplasm of rat liver». Biochem. J., 115, 4, 1969, pàg. 609–19. PMID: 4391039.
- ↑ Katoh A, Uenohara K, Akita M, Hashimoto T «Early steps in the biosynthesis of NAD in Arabidopsis start with aspartate and occur in the plastid». Plant Physiol., 141, 3, 2006, pàg. 851–7. DOI: 10.1104/p.106.081091. PMC: 1489895. PMID: 16698895.
- ↑ Foster JW, Moat AG «Nicotinamide adenine dinucleotide biosynthesis and pyridine nucleotide cycle metabolism in microbial systems». Microbiol. Rev., 44, 1, 01-03-1980, pàg. 83–105. PMC: 373235. PMID: 6997723.
- ↑ Magni G, Orsomando G, Raffaelli N «Structural and functional properties of NAD kinase, a key enzyme in NADP biosynthesis». Mini reviews in medicinal chemistry, 6, 7, 2006, pàg. 739–46. DOI: 10.2174/138955706777698688. PMID: 16842123.
- ↑ Sakuraba H, Kawakami R, Ohshima T «First archaeal inorganic polyphosphate/ATP-dependent NAD kinase, from hyperthermophilic archaeon Pyrococcus horikoshii: cloning, expression, and characterization». Appl. Environ. Microbiol., 71, 8, 2005, pàg. 4352–8. DOI: 10.1128/AEM.71.8.4352-4358.2005. PMC: 1183369. PMID: 16085824.
- ↑ Raffaelli N, Finaurini L, Mazzola F, et al. «Characterization of Mycobacterium tuberculosis NAD kinase: functional analysis of the full-length enzyme by site-directed mutagenesis». Biochemistry, 43, 23, 2004, pàg. 7610–7. DOI: 10.1021/bi049650w. PMID: 15182203.
- ↑ Tempel W, Rabeh WM, Bogan KL, et al. «Nicotinamide riboside kinase structures reveal new pathways to NAD+». PLoS Biol., 5, 10, 2007, pàg. e263. DOI: 10.1371/journal.pbio.0050263. PMC: 1994991. PMID: 17914902.
- ↑ Anderson RM, Bitterman KJ, Wood JG, et al. «Manipulation of a nuclear NAD+ salvage pathway delays aging without altering steady-state NAD+ levels». J. Biol. Chem., 277, 21, 2002, pàg. 18881–90. Arxivat de l'original el 2020-04-13. DOI: 10.1074/jbc.M111773200. PMID: 11884393 [Consulta: 15 desembre 2009]. Arxivat 2020-04-13 a Wayback Machine.
- ↑ Billington RA, Travelli C, Ercolano E, et al. «Characterization of NAD Uptake in Mammalian Cells». J. Biol. Chem., 283, 10, 2008, pàg. 6367–74. Arxivat de l'original el 2020-05-28. DOI: 10.1074/jbc.M706204200. PMID: 18180302 [Consulta: 15 desembre 2009]. Arxivat 2020-05-28 a Wayback Machine.
- ↑ Henderson LM «Niacin». Annu. Rev. Nutr., 3, 1983, pàg. 289–307. DOI: 10.1146/annurev.nu.03.070183.001445. PMID: 6357238.
- ↑ 29,0 29,1 Rongvaux A, Andris F, Van Gool F, Leo O «Reconstructing eukaryotic NAD metabolism». Bioessays, 25, 7, 2003, pàg. 683–90. DOI: 10.1002/bies.10297. PMID: 12815723.
- ↑ Ma B, Pan SJ, Zupancic ML, Cormack BP «Assimilation of NAD(+) precursors in Candida glabrata». Mol. Microbiol., 66, 1, 2007, pàg. 14–25. DOI: 10.1111/j.1365-2958.2007.05886.x.
- ↑ Reidl J, Schlör S, Kraiss A, Schmidt-Brauns J, Kemmer G, Soleva E «NADP and NAD utilization in Haemophilus influenzae». Mol. Microbiol., 35, 6, 2000, pàg. 1573–81. DOI: 10.1046/j.1365-2958.2000.01829.x. PMID: 10760156.
- ↑ Gerdes SY, Scholle MD, D'Souza M, et al. «From genetic footprinting to antimicrobial drug targets: examples in cofactor biosynthetic pathways». J. Bacteriol., 184, 16, 2002, pàg. 4555–72. DOI: 10.1128/JB.184.16.4555-4572.2002. PMC: 135229. PMID: 12142426.
- ↑ Senkovich O, Speed H, Grigorian A, et al. «Crystallization of three key glycolytic enzymes of the opportunistic pathogen Cryptosporidium parvum». Biochim. Biophys. Acta, 1750, 2, 2005, pàg. 166–72. PMID: 15953771.
- ↑ «Enzyme Nomenclature, Recommendations for enzyme names from the Nomenclature Committee of the International Union of Biochemistry and Molecular Biology». [Consulta: 6 desembre 2007].
- ↑ «NiceZyme View of ENZYME: EC 1.6.5.3». Expasy. [Consulta: 16 desembre 2007].
- ↑ Lesk AM «NAD-binding domains of dehydrogenases». Curr. Opin. Struct. Biol., 5, 6, 1995, pàg. 775–83. DOI: 10.1016/0959-440X(95)80010-7. PMID: 8749365.
- ↑ 37,0 37,1 Rao S, Rossmann M «Comparison of super-secondary structures in proteins». J Mol Biol, 76, 2, 1973, pàg. 241–56. DOI: 10.1016/0022-2836(73)90388-4. PMID: 4737475.
- ↑ Goto M, Muramatsu H, Mihara H, et al. «Crystal structures of Delta1-piperideine-2-carboxylate/Delta1-pyrroline-2-carboxylate reductase belonging to a new family of NAD(P)H-dependent oxidoreductases: conformational change, substrate recognition, and stereochemistry of the reaction». J. Biol. Chem., 280, 49, 2005, pàg. 40875–84. Arxivat de l'original el 2008-06-11. DOI: 10.1074/jbc.M507399200. PMID: 16192274 [Consulta: 15 desembre 2009]. Arxivat 2008-06-11 a Wayback Machine.
- ↑ Bellamacina CR «The nicotinamide dinucleotide binding motif: a comparison of nucleotide binding proteins». FASEB J., 10, 11, 01-09-1996, pàg. 1257–69. PMID: 8836039.
- ↑ Carugo O, Argos P «NADP-dependent enzymes. I: Conserved stereochemistry of cofactor binding». Proteins, 28, 1, 1997, pàg. 10–28. DOI: 10.1002/(SICI)1097-0134(199705)28:1<10::AID-PROT2>3.0.CO;2-N. PMID: 9144787.
- ↑ Vickers TJ, Orsomando G, de la Garza RD, et al. «Biochemical and genetic analysis of methylenetetrahydrofolate reductase in Leishmania metabolism and virulence». J. Biol. Chem., 281, 50, 2006, pàg. 38150–8. Arxivat de l'original el 2008-10-13. DOI: 10.1074/jbc.M608387200. PMID: 17032644 [Consulta: 15 desembre 2009]. Arxivat 2008-10-13 a Wayback Machine.
- ↑ Bakker BM, Overkamp KM, van Maris AJ, et al. «Stoichiometry and compartmentation of NADH metabolism in Saccharomyces cerevisiae». FEMS Microbiol. Rev., 25, 1, 2001, pàg. 15–37. DOI: 10.1111/j.1574-6976.2001.tb00570.x. PMID: 11152939.
- ↑ Rich PR «The molecular machinery of Keilin's respiratory chain». Biochem. Soc. Trans., 31, Pt 6, 2003, pàg. 1095–105. DOI: 10.1042/BST0311095. PMID: 14641005.
- ↑ Heineke D, Riens B, Grosse H, et al. «Redox Transfer across the Inner Chloroplast Envelope Membrane». Plant Physiol, 95, 4, 1991, pàg. 1131–1137. DOI: 10.1104/p.95.4.1131. PMID: 16668101.
- ↑ 45,0 45,1 Nicholls DG; Ferguson SJ. Bioenergetics 3. 1st. Academic Press, 2002. ISBN 0-125-18121-3.
- ↑ Sistare FD, Haynes RC «The interaction between the cytosolic pyridine nucleotide redox potential and gluconeogenesis from lactate/pyruvate in isolated rat hepatocytes. Implications for investigations of hormone action». J. Biol. Chem., 260, 23, 15-10-1985, pàg. 12748–53. Arxivat de l'original el 12 d’abril 2008. PMID: 4044607 [Consulta: 15 desembre 2009]. Arxivat 12 April 2008[Date mismatch] a Wayback Machine.
- ↑ Freitag A, Bock E «Energy conservation in Nitrobacter». FEMS Microbiology Letters, 66, 1–3, 1990, pàg. 157–62. DOI: 10.1111/j.1574-6968.1990.tb03989.x.
- ↑ Starkenburg SR, Chain PS, Sayavedra-Soto LA, et al. «Genome sequence of the chemolithoautotrophic nitrite-oxidizing bacterium Nitrobacter winogradskyi Nb-255». Appl. Environ. Microbiol., 72, 3, 2006, pàg. 2050–63. DOI: 10.1128/AEM.72.3.2050-2063.2006. PMID: 16517654.
- ↑ Ziegler M «New functions of a long-known molecule. Emerging roles of NAD in cellular signaling». Eur. J. Biochem., 267, 6, 2000, pàg. 1550–64. DOI: 10.1046/j.1432-1327.2000.01187.x. PMID: 10712584.
- ↑ Chen, Y Grace; Walter E Kowtoniuk, Isha Agarwal, Yinghua Shen, David R Liu «LC/MS analysis of cellular RNA reveals NAD-linked RNA». Nat Chem Biol, 5, 12, 2009-12, pàg. 879–881. DOI: 10.1038/nchembio.235.
- ↑ 51,0 51,1 Diefenbach J, Bürkle A «Introduction to poly(ADP-ribose) metabolism». Cell. Mol. Life Sci., 62, 7–8, 2005, pàg. 721–30. DOI: 10.1007/s00018-004-4503-3. PMID: 15868397.
- ↑ Berger F, Ramírez-Hernández MH, Ziegler M «The new life of a centenarian: signaling functions of NAD(P)». Trends Biochem. Sci., 29, 3, 2004, pàg. 111–8. DOI: 10.1016/j.tibs.2004.01.007. PMID: 15003268.
- ↑ Corda D, Di Girolamo M «Functional aspects of protein mono-ADP-ribosylation». EMBO J., 22, 9, 2003, pàg. 1953–8. DOI: 10.1093/emboj/cdg209. PMC: 156081. PMID: 12727863.
- ↑ 54,0 54,1 Burkle A «Poly(ADP-ribose). The most elaborate metabolite of NAD+». FEBS J., 272, 18, 2005, pàg. 4576–89. DOI: 10.1111/j.1742-4658.2005.04864.x. PMID: 16156780.
- ↑ Seman M, Adriouch S, Haag F, Koch-Nolte F «Ecto-ADP-ribosyltransferases (ARTs): emerging actors in cell communication and signaling». Curr. Med. Chem., 11, 7, 2004, pàg. 857–72. DOI: 10.2174/0929867043455611. PMID: 15078170.
- ↑ Guse AH «Biochemistry, biology, and pharmacology of cyclic adenosine diphosphoribose (cADPR)». Curr. Med. Chem., 11, 7, 2004, pàg. 847–55. DOI: 10.2174/0929867043455602. PMID: 15078169.
- ↑ Guse AH «Regulation of calcium signaling by the second messenger cyclic adenosine diphosphoribose (cADPR)». Curr. Mol. Med., 4, 3, 2004, pàg. 239–48. DOI: 10.2174/1566524043360771. PMID: 15101682.
- ↑ Guse AH «Second messenger function and the structure-activity relationship of cyclic adenosine diphosphoribose (cADPR)». FEBS J., 272, 18, 2005, pàg. 4590–7. DOI: 10.1111/j.1742-4658.2005.04863.x. PMID: 16156781.
- ↑ North B, Verdin E «Sirtuins: Sir2-related NAD-dependent protein deacetylases». Genome Biol, 5, 5, 2004, pàg. 224. DOI: 10.1186/gb-2004-5-5-224. PMC: 416462. PMID: 15128440.
- ↑ Blander G, Guarente L «The Sir2 family of protein deacetylases». Annu. Rev. Biochem., 73, 2004, pàg. 417–35. DOI: 10.1146/annurev.biochem.73.011303.073651. PMID: 15189148.
- ↑ Trapp J, Jung M «The role of NAD+ dependent histone deacetylases (sirtuins) in ageing». Curr Drug Targets, 7, 11, 2006, pàg. 1553–60. PMID: 17100594.
- ↑ Wilkinson A, Day J, Bowater R «Bacterial DNA ligases». Mol. Microbiol., 40, 6, 2001, pàg. 1241–8. DOI: 10.1046/j.1365-2958.2001.02479.x. PMID: 11442824.
- ↑ Schär P, Herrmann G, Daly G, Lindahl T «A newly identified DNA ligase of Saccharomyces cerevisiae involved in RAD52-independent repair of DNA double-strand breaks». Genes and Development, 11, 15, 1997, pàg. 1912–24. DOI: 10.1101/gad.11.15.1912. PMID: 9271115.
- ↑ Sauve AA «NAD+ and vitamin B3: from metabolism to therapies». The Journal of pharmacology and experimental therapeutics, 324, 3, març 2008, pàg. 883–93. DOI: 10.1124/jpet.107.120758. PMID: 18165311.
- ↑ Khan JA, Forouhar F, Tao X, Tong L «Nicotinamide adenine dinucleotide metabolism as an attractive target for drug discovery». Expert Opin. Ther. Targets, 11, 5, 2007, pàg. 695–705. DOI: 10.1517/14728222.11.5.695. PMID: 17465726.
- ↑ Kaneko S, Wang J, Kaneko M, et al «Protecting axonal degeneration by increasing nicotinamide adenine dinucleotide levels in experimental autoimmune encephalomyelitis models». J. Neurosci., 26, 38, 2006, pàg. 9794–804. DOI: 10.1523/JNEUROSCI.2116-06.2006. PMID: 16988050.
- ↑ Swerdlow RH «Is NADH effective in the treatment of Parkinson's disease?». Drugs Aging, 13, 4, 1998, pàg. 263–8. DOI: 10.2165/00002512-199813040-00002. PMID: 9805207.
- ↑ Timmins GS, Deretic V «Mechanisms of action of isoniazid». Mol. Microbiol., 62, 5, 2006, pàg. 1220–7. Arxivat de l'original el 2007-12-22. DOI: 10.1111/j.1365-2958.2006.05467.x. PMID: 17074073 [Consulta: 15 desembre 2009]. Arxivat 2007-12-22 a Wayback Machine.
- ↑ Rawat R, Whitty A, Tonge PJ «The isoniazid-NAD adduct is a slow, tight-binding inhibitor of InhA, the Mycobacterium tuberculosis enoyl reductase: adduct affinity and drug resistance». Proc. Natl. Acad. Sci. U.S.A., 100, 24, 2003, pàg. 13881–6. DOI: 10.1073/pnas.2235848100. PMID: 14623976.
- ↑ Argyrou A, Vetting MW, Aladegbami B, Blanchard JS «Mycobacterium tuberculosis dihydrofolate reductase is a target for isoniazid». Nat. Struct. Mol. Biol., 13, 5, 2006, pàg. 408–13. DOI: 10.1038/nsmb1089. PMID: 16648861.
- ↑ 71,0 71,1 Pankiewicz KW, Patterson SE, Black PL, et al. «Cofactor mimics as selective inhibitors of NAD-dependent inosine monophosphate dehydrogenase (IMPDH)—the major therapeutic target». Curr. Med. Chem., 11, 7, 2004, pàg. 887–900. DOI: 10.2174/0929867043455648. PMID: 15083807.
- ↑ Franchetti P, Grifantini M «Nucleoside and non-nucleoside IMP dehydrogenase inhibitors as antitumor and antiviral agents». Curr. Med. Chem., 6, 7, 1999, pàg. 599–614. PMID: 10390603.
- ↑ Kim EJ, Um SJ «SIRT1: roles in aging and cancer». BMB Rep, 41, 11, 2008, pàg. 751–6. PMID: 19017485.
- ↑ Valenzano DR, Terzibasi E, Genade T, Cattaneo A, Domenici L, Cellerino A «Resveratrol prolongs lifespan and retards the onset of age-related markers in a short-lived vertebrate». Curr. Biol., 16, 3, 2006, pàg. 296–300. DOI: 10.1016/j.cub.2005.12.038. PMID: 16461283.
- ↑ Howitz KT, Bitterman KJ, Cohen HY, et al. «Small molecule activators of sirtuins extend Saccharomyces cerevisiae lifespan». Nature, 425, 6954, 2003, pàg. 191–6. DOI: 10.1038/nature01960. PMID: 12939617.
- ↑ Wood JG, Rogina B, Lavu S, et al. «Sirtuin activators mimic caloric restriction and delay ageing in metazoans». Nature, 430, 7000, 2004, pàg. 686–9. DOI: 10.1038/nature02789. PMID: 15254550.
- ↑ Rizzi M, Schindelin H «Structural biology of enzymes involved in NAD and molybdenum cofactor biosynthesis». Curr. Opin. Struct. Biol., 12, 6, 2002, pàg. 709–20. DOI: 10.1016/S0959-440X(02)00385-8. PMID: 12504674.
- ↑ Begley TP, Kinsland C, Mehl RA, Osterman A, Dorrestein P «The biosynthesis of nicotinamide adenine dinucleotides in bacteria». Vitam. Horm., 61, 2001, pàg. 103–19. DOI: 10.1016/S0083-6729(01)61003-3. PMID: 11153263.
- ↑ Harden, A; Young, WJ «The Alcoholic Ferment of Yeast-Juice». Proceedings of the Royal Society of London, 78, Series B, Containing Papers of a Biological Character, October 1906, pàg. 369–375.
- ↑ «Fermentation of sugars and fermentative enzymes» (PDF). Nobel Lecture, 23 May 1930. Nobel Foundation. [Consulta: 30 setembre 2007].
- ↑ Warburg O, Christian W. «Pyridin, the hydrogen-transferring component of the fermentation enzymes (pyridine nucleotide)». Biochemische Zeitschrift, 287, 1936, pàg. 291.
- ↑ Elvehjem CA, Madden RJ, Strong FM, Woolley DW. «The isolation and identification of the anti-black tongue factor» (PDF). J. Biol. Chem., 123, 1, 1938, pàg. 137–49. Arxivat de l'original el 2009-03-26 [Consulta: 15 desembre 2009]. Arxivat 2009-03-26 a Wayback Machine.
- ↑ Axelrod AE, Madden RJ, Elvehjem CA, «The effect of a nicotinic acid deficiency upon the coenzyme I content of animal tissues» (PDF). J. Biol. Chem., 131, 1, 1939, pàg. 85–93. Arxivat de l'original el 2009-03-26 [Consulta: 15 desembre 2009]. Arxivat 2009-03-26 a Wayback Machine.
- ↑ Kornberg, A. «The participation of inorganic pyrophosphate in the reversible enzymatic synthesis of diphosphopyridine nucleotide» (PDF). J. Biol. Chem., 176, 3, 1948, pàg. 1475–76. Arxivat de l'original el 2009-03-26 [Consulta: 15 desembre 2009]. Arxivat 2009-03-26 a Wayback Machine.
- ↑ Friedkin M, Lehninger AL. «Esterification of inorganic phosphate coupled to electron transport between dihydrodiphosphopyridine nucleotide and oxygen». J. Biol. Chem., 178, 2, 01-04-1949, pàg. 611–23.
- ↑ Preiss J, Handler P. «Biosynthesis of diphosphopyridine nucleotide. I. Identification of intermediates». J. Biol. Chem., 233, 2, 01-08-1958, pàg. 488–92. Arxivat de l'original el 14 de desembre 2007. PMID: 13563526 [Consulta: 15 desembre 2009]. Arxivat 14 de desembre 2007 a Wayback Machine.
- ↑ Preiss J, Handler P. «Biosynthesis of diphosphopyridine nucleotide. II. Enzymatic aspects». J. Biol. Chem., 233, 2, 01-08-1958, pàg. 493–500. Arxivat de l'original el 13 d’abril 2020. PMID: 13563527 [Consulta: 15 desembre 2009]. Arxivat 13 April 2020[Date mismatch] a Wayback Machine.
- ↑ Chambon P, Weill JD, Mandel P «Nicotinamide mononucleotide activation of new DNA-dependent polyadenylic acid synthesizing nuclear enzyme». Biochem. Biophys. Res. Commun., 11, 1963, pàg. 39–43. DOI: 10.1016/0006-291X(63)90024-X. PMID: 14019961.
- ↑ Clapper DL, Walseth TF, Dargie PJ, Lee HC «Pyridine nucleotide metabolites stimulate calcium release from sea urchin egg microsomes desensitized to inositol trisphosphate». J. Biol. Chem., 262, 20, 15-07-1987, pàg. 9561–8. Arxivat de l'original el 14 de desembre 2007. PMID: 3496336 [Consulta: 15 desembre 2009]. Arxivat 14 de desembre 2007 a Wayback Machine.
- ↑ Imai S, Armstrong CM, Kaeberlein M, Guarente L «Transcriptional silencing and longevity protein Sir2 is an NAD-dependent histone deacetylase». Nature, 403, 6771, 2000, pàg. 795–800. DOI: 10.1038/35001622. PMID: 10693811.
Bibliografia[modifica]
- Funció
- Nelson DL; Cox MM. Lehninger Principles of Biochemistry. 4th. W. H. Freeman, 2004. ISBN 0-716-74339-6.
- Bugg, T. Introduction to Enzyme and Coenzyme Chemistry. 2nd. Blackwell Publishing Limited, 2004. ISBN 1-40511-452-5.
- Lee HC. Cyclic ADP-Ribose and NAADP: Structure, Metabolism and Functions. Kluwer Academic Publishers, 2002. ISBN 1-40207-281-3.
- Història
- Cornish-Bowden, Athel. New Beer in an Old Bottle. Eduard Buchner and the Growth of Biochemical Knowledge.. Valencia: Universitat de Valencia, 1997. ISBN 84-370-3328-4 [Consulta: 15 desembre 2009]. Arxivat 2010-12-13 a Wayback Machine., A history of early enzymology.
- Williams, Henry Smith, 1863–1943. Modern Development of the Chemical and Biological Sciences. IV. Nova York: Harper and Brothers, 1904 (A History of Science: in Five Volumes)., A textbook from the 19th century.
Enllaços externs[modifica]
| A Wikimedia Commons hi ha contingut multimèdia relatiu a: Dinucleòtid de nicotinamida i adenina |
- NAD Animation (Flash Required)
- β-Nicotinamide adenine dinucleotide (NAD+, oxidized) and NADH (reduced) Chemical data sheet from Sigma-Aldrich
- NAD+, NADH and NAD synthesis pathway at the MetaCyc database
- List of oxidoreductases a la base de dades Swiss-Prot

